Producción de proteínas recombinantes de Plasmodium falciparum en Escherichia coli
Resumen
Introducción. La producción de proteínas recombinantes es fundamental para el estudio funcional de las proteínas de Plasmodium falciparum. Sin embargo, las proteínas recombinantes de P. falciparum están entre las más difíciles de expresar y, cuando lo hacen, usualmente se agregan dentro de cuerpos de inclusión insolubles.
Objetivo. Evaluar la producción de cuatro proteínas de P. falciparum usando como sistema de expresión dos cepas de Escherichia coli genéticamente modificadas para favorecer la producción de proteínas heterólogas y establecer una reserva de proteínas recombinantes puras y solubles, y producir anticuerpos policlonales a partir de ellas.
Materiales y métodos. Las proteínas recombinantes, las cuales correspondían a secuencias parciales de PfMyoA (Miosina-A) y PfGAP50 (proteína-asociada a glideosoma de 50 kDa) y a las secuencias completas de PfMTIP (proteína de interacción con miosina-A) y PfGAP45 (proteína asociada a glideosoma de 45 kDa), fueron expresadas como proteínas de fusión con la glutatión S-transferasa y luego purificadas y usadas para producir anticuerpos policlonales en ratón.
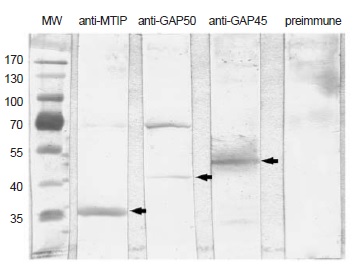
Resultados. La expresión de las proteínas recombinantes fue mucho más eficiente en la cepa BL21-CodonPlus (la cual expresa tRNAs escasos en las bacterias silvestres), que en la cepa BL21-pG-KJE8. Por el contrario, aunque la cepa BL21-pG-KJE sobreexpresa chaperonas, no redujo la formación de cuerpos de inclusión.
Conclusión. El uso de cepas de E. coli genéticamente modificadas fue fundamental para alcanzar altos niveles de expresión de las cuatro proteínas recombinantes evaluadas y permitió obtener dos de ellas en forma soluble. La estrategia utilizada permitió expresar cuatro proteínas recombinantes de P. falciparum en cantidad suficiente para inmunizar ratones y producir anticuerpos policlonales y, además, conservar proteína pura y soluble de dos de ellas para ensayos futuros.
Descargas
Referencias bibliográficas
World Health Organization. World Malaria Report 2014: Summary. Accessed: April 1st, 2015. Available from: http://apps.who.int/iris/bitstream/10665/160458/1/WHO_HTM_GMP_2015.2_eng.pdf?ua=1.
Cowman AF, Crabb BS. Invasion of red blood cells by malaria parasites. Cell. 2006;124:755-66. http://dx.doi.org/10.1016/j.cell.2006.02.006.
Frénal K, Polonais V, Marq JB, Stratmann R, Limenitakis J, Soldati-Favre D. Functional dissection of the apicomplexan glideosome molecular architecture. Cell Host Microbe. 2010;8:343-57. http://dx.doi.org/10.1016/j.chom.2010.09.002.
Baum J, Richard D, Healer J, Rug M, Krnajski Z, Gilberger TW, et al. A conserved molecular motor drives cell invasion and gliding motility across malaria life cycle stages and other apicomplexan parasites. J Biol Chem. 2006;281:5197-208. http://dx.doi.org/10.1074/jbc.M509807200.
Overton TW. Recombinant protein production in bacterial hosts. Drug Discov Today. 2014;19:590-601. http://dx.doi.org/10.1016/j.drudis.2013.11.008.
Horrocks P, Bowman S, Kyes S, Waters AP, Craig A. Entering the post-genomic era of malaria research. Bull WHO. 2000;78:1424-37.
Yadava A, Ockenhouse CF. Effect of codon optimisation on expression levels of a functionally folded malaria vaccine candidate in prokaryotic and eukaryotic expression system. Infect Immun. 2003;71:4961-9. http://dx.doi.org/10.1128/IAI.71.9.4961-4969.2003.
Flick K, Ahuja S, Chene A, Bejarano MT, Chen Q. Optimized expression of Plasmodium falciparum erythrocyte membrane protein 1 domains in Escherichia coli. Malar J. 2004;3:50. http://dx.doi.org/10.1186/1475-2875-3-50.
Villaverde A, Carrio MM. Protein aggregation in recombinant bacteria: Biological role of inclusion bodies. Biotechnol Lett. 2003;25:1385-95. http://dx.doi.org/10.1023/A:1025024104862.
Wasserman M, Contreras J, Pinilla G, Rojas MO, Páez A, Caminos E. Plasmodium falciparum: Characterization of a 0.7-kbp, moderately repetitive sequence. Exp Parasitol. 1995;81:165-71. http://dx.doi.org/10.1006/expr.1995.1105.
Sørensen HP, Mortensen KK. Soluble expression of recombinant proteins in the cytoplasm of Escherichia coli. Microb Cell Fact. 2005;4:1. http://dx.doi.org/10.1186/1475-2859-4-1.
Scheer JM, Ryan CA. A method for the quantitative recovery of proteins from polyacrylamide gels. Anal Biochem. 2001; 298:130-2. http://dx.doi.org/10.1006/abio.2001.5384.
Harlow E, Lane D. Antibodies: A laboratory manual. First edition. New York: Cold Spring Harbor Laboratory Press; 1988. p. 67, 92-120. http://dx.doi.org/10.1002/jobm.3620300304.
Jonasson P, Liljeqvist S, Nygren PA, Ståhl S. Genetic design for facilitated production and recovery of recombinant proteins in Escherichia coli. Biotechnol Appl Biochem. 2002;35:91-105. http://dx.doi.org/10.1042/BA20010099.
Donovan RS, Robinson CW, Glick BR. Optimizing inducer and culture conditions for expression of foreign proteins under the control of the lac promoter. J Ind Microbiol. 1996;16:145-54. http://dx.doi.org/10.1007/BF01569997.
Mehlin C, Boni E, Buckner FS, Engel L, Feist T, Gelb MH, et al. Heterologous expression of proteins from Plasmodium falciparum: Results from 1000 genes. Mol Biochem Parasitol. 2006;148:144-60. http://dx.doi.org/10.1016/j.molbiopara.2006.03.011.
Vedadi M, Lew J, Artz J, Amani M, Zhao Y, Dong A, et al. Genome-scale protein expression and structural biology of Plasmodium falciparum and related Apicomplexan organisms. Mol Biochem Parasitol. 2007;151:100-10. http://dx.doi.org/10.1016/j.molbiopara.2006.10.011.
Armstrong DJ, Roman A. The anomalous electrophoretic behavior of the human papillomavirus type 16 E7 protein is due to the high content of acidic amino acid residues. Biochem Biophys Res Commun. 1993;192:1380-7. http://dx.doi.org/10.1006/bbrc.1993.1569.
Iakoucheva LM, Kimzey AL, Masselon CD, Smith RD, Dunker AK, Ackerman EJ. Aberrant mobility phenomena of the DNA repair protein XPA. Protein Sci. 2001;10:1353-62. http://dx.doi.org/10.1110/ps.ps.40101.
Shi W, Huang Y, Sutton-Smith M, Tissot B, Panico M, Morris HR, et al. A filovirus-unique region of Ebola virus nucleoprotein confers aberrant migration and mediates its incorporation into virions. J Virol. 2008;82:6190-9. http://dx.doi.org/10.1128/JVI.02731-07.
Jones ML, Kitson EL, Rayner JC. Plasmodium falciparum erythrocyte invasion: A conserved myosin associated complex. Mol Biochem Parasitol. 2006;147:74-84. http://dx.doi.org/10.1016/j.molbiopara.2006.01.009.
Rees-Channer RR, Martin SR, Green JL, Bowyer PW, Grainger M, Molloy JE, et al. Dual acylation of the 45 kDa gliding-associated protein (GAP45) in Plasmodium falciparum merozoites. Mol Biochem Parasitol. 2006;149:113-6. http://dx.doi.org/10.1016/j.molbiopara.2006.04.008.
Baca AM, Hol WG. Overcoming codon bias: A method for high-level overexpression of Plasmodium and other AT-rich parasite genes in Escherichia coli. Int J Parasitol. 2000;30:113-8. http://dx.doi.org/10.1016/S0020-7519(00)00019-9.
Karmodiya K, Srivastav RK, Surolia N. Production and purification of refolded recombinant Plasmodium falciparum beta-ketoacyl-ACP reductase from inclusion bodies. Protein Expr Purif. 2005;42:131-6. http://dx.doi.org/10.1016/j.pep.2005.02.008.
Carstens P. Use of tRNA-supplemented host strains for expression of heterologous genes in E. coli. In: Vaillancourt PE, editor. E. coli gene expression protocols. Totowa, NJ: Humana Press; 2003. p. 225-33. http://dx.doi.org/10.1385/1-59259-301-1:225.
Goldman E, Rosenberg AH, Zubay G, Studier FW. Consecutive low-usage leucine codons block translation only when near the 5' end of a message in Escherichia coli. J Mol Biol. 1995;245:467-73. http://dx.doi.org/10.1006/jmbi.1994.0038.
Chen GF, Inouye M. Suppression of the negative effect of minor arginine codons on gene expression; preferential usage of minor codons within the first 25 codons of the Escherichia coli genes. Nucleic Acids Res. 1990;18:1465-73. http://dx.doi.org/10.1093/nar/18.6.1465.
Rosano GL, Ceccarelli EA. Rare codon content affects the solubility of recombinant proteins in a codon bias-adjusted Escherichia coli strain. Microb Cell Fact. 2009;8:41. http://dx.doi.org/10.1186/1475-2859-8-41.
Schumann W, Ferreira LC. Production of recombinant proteins in Escherichia coli. Genet Mol Biol. 2004;27:442-53. http://dx.doi.org/10.1590/S1415-47572004000300022.
Barth S, Huhn M, Matthey B, Klimka A, Galinski EA, Engert A. Compatible-solute-supported periplasmic expression of functional recombinant proteins under stress conditions. Appl Environ Microbiol. 2000;66:1572-9. http://dx.doi.org/10.1128/AEM.66.4.1572-1579.2000.
Schäffner J, Winter J, Rudolph R, Schwarz E. Cosecretion of chaperones and low-molecular-size medium additives increases the yield of recombinant disulfide-bridged proteins. Appl Environ Microbiol. 2001;67:3994-4000. http://dx.doi.org/10.1128/AEM.67.9.3994-4000.2001.
Choi JH, Lee SY. Secretory and extracellular production of recombinant proteins using Escherichia coli. Appl Microbiol Biotechnol. 2004;64:625-35. http://dx.doi.org/10.1007/s00253-004-1559-9.
Wall JG, Plückthun A. Effects of overexpressing folding modulators on the in vivo folding of heterologous proteins in Escherichia coli. Curr Opin Biotechnol. 1995;6:507-16. http://dx.doi.org/10.1016/0958-1669(95)80084-0.
Martínez-Alonso M, García-Fruitós E, Ferrer-Miralles N, Rinas U, Villaverde A. Side effects of chaperone gene co-expression in recombinant protein production. Microb Cell Fact. 2010;9:64. http://dx.doi.org/10.1186/1475-2859-9-64.
Algunos artículos similares:
- Ana María Vásquez, Felipe Sanín, Luis Gonzalo Álvarez, Alberto Tobón, Alexandra Ríos, Silvia Blair, Estudio piloto de la eficacia y de los efectos sobre los gametocitos del esquema artesunato-mefloquina-primaquina para la malaria por Plasmodium falciparum , Biomédica: Vol. 29 Núm. 2 (2009)
- Amanda Maestre, Jaime Carmona-Fonseca, Amanda Maestre, Alta frecuencia de mutaciones puntuales en pfcrt de Plasmodium falciparum y emergencia de nuevos haplotipos mutantes en Colombia , Biomédica: Vol. 28 Núm. 4 (2008)
- Silvia Blair, Ana Mercedes Rada, Carolina Moreno, Exitoso cultivo in vitro de gametocitos de Plasmodium falciparum , Biomédica: Vol. 28 Núm. 4 (2008)
- Jaime Carmona-Fonseca, Eliana Arango, Silvia Blair, Gametocitemia en malaria por Plasmodium falciparum tratada con amodiaquina o artesunato , Biomédica: Vol. 28 Núm. 2 (2008)
- Silvia Blair, Eliana Arango, Jaime Carmona Fonseca, Susceptibilidad in vitro de aislamientos colombianos de Plasmodium falciparum a diferentes antipalúdicos , Biomédica: Vol. 28 Núm. 2 (2008)
- John Alexander Galindo, Fabio Aníbal Cristiano, Angélica Knudson, Rubén Santiago Nicholls, Ángela Patricia Guerra, Mutaciones puntuales en los genes dhfr y dhps de Plasmodium falciparum de tres regiones endémicas , Biomédica: Vol. 30 Núm. 1 (2010)
- Nohora Marcela Mendoza, Marisol García, Liliana Jazmín Cortés, Claudia Vela, Rigoberto Erazo, Pilar Pérez, Olga Lucía Ospina, Javier Darío Burgos, Evaluación de dos pruebas rápidas [NOW® ICT Malaria Pf/Pv y OptiMAL®] para el diagnóstico de paludismo en Tumaco, Colombia , Biomédica: Vol. 27 Núm. 4 (2007)
- Angélica Knudson, Rubén Santiago Nicholls, Ángela Patricia Guerra, Ricardo Sánchez, Perfiles clínicos del paludismo no complicado por Plasmodium falciparum en Córdoba, Colombia , Biomédica: Vol. 27 Núm. 4 (2007)
- Adriana Pabón, Gonzalo Álvarez, Jorge Yánez, Carlos Céspedes, Yensa Rodríguez, Ángela Restrepo, Silvia Blair, Evaluación de la prueba rápida inmunocromatográfica Binax NOW® ICT Pf/Pv para el diagnóstico del paludismo en un área endémica de Colombia , Biomédica: Vol. 27 Núm. 2 (2007)
- Sandra Milena Barrera, Manuel Alberto Pérez, Angélica Knudson, Rubén Santiago Nicholls, Ángela Patricia Guerra, Genotipificación de Plasmodium falciparum por PCR múltiple por medio de los genes msp1, msp2 y glurp, en cuatro localidades de Colombia , Biomédica: Vol. 30 Núm. 4 (2010)
| Estadísticas de artículo | |
|---|---|
| Vistas de resúmenes | |
| Vistas de PDF | |
| Descargas de PDF | |
| Vistas de HTML | |
| Otras vistas | |

























