Caracterización molecular de enterobacterias multirresistentes en dos departamentos de la selva peruana
Resumen
Introducción. La aparición de enterobacterias multirresistentes y productoras de betalactamasas de espectro extendido (BLEE) en pacientes de consulta externa con infecciones urinarias, representa un problema de salud pública en Perú.
Objetivos. Caracterizar molecularmente enterobacterias multirresistentes aisladas de pacientes con diagnóstico de infección urinaria y procedentes de dos departamentos de la selva peruana.
Materiales y métodos. Se hizo un estudio descriptivo, observacional y retrospectivo de 61 aislamientos de urocultivo procedentes de la selva peruana durante 2017 y 2018. Los perfiles de resistencia se identificaron utilizando el sistema automatizado MicroScan™ y para la detección de los genes blaTEM, blaCTX-M, blaSHV se empleó una reacción en cadena de la polimerasa (PCR) convencional.
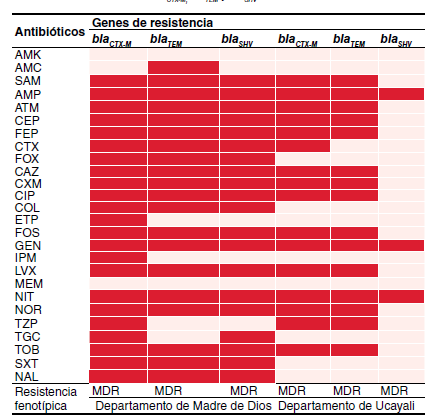
Resultados. Las enterobacterias positivas para BLEE más frecuentes por departamento fueron Escherichia coli en Madre de Dios (25 %, 10/40) y Ucayali (76,2 %, 16/21). En ambos departamentos, el gen blaCTX-M fue el más frecuente (25/61; 41 %), seguido por blaTEM (15/61; 24,6 %) y blaSHV (10/61; 16,4 %). En el perfil de sensibilidad antimicrobiana, se detectó 72,6 % de resistencia contra ampicilina, 82,3 % contra cefalotina y 88,7 % contra nitrofurantoína.
Conclusiones. El porcentaje de cepas de enterobacterias multirresistentes productoras de BLEE en ambos departamentos fue del 57,4 % y el gen bla CTX-M fue el más frecuente.
Descargas
Referencias bibliográficas
Organización Mundial de la Salud. Resistencia a los antibióticos 2021. Fecha de consulta: 3 de mayo del 2021. Disponible en: https://bit.ly/3h0V2Ch
Yábar MN, Curi-Pesantes B, Torres CA, Calderón-Anyosa R, Riveros M, Ochoa TJ. Multiresistance and factors associated with the presence of extended-spectrum betalactamases in Escherichia coli strains isolated from urine culture. Rev Perú Med Exp Salud Pública. 2017;34:660-5. https://doi.org/10.17843/rpmesp.2017.344.2922
Sbiti M, Lahmadi K, Louzi L. Profil épidémiologique des entérobactéries uropathogènes productrices de bêta-lactamases à spectre élargi. Pan Afr Med J. 2017;28:29. https://doi.org/10.11604/pamj.2017.28.29.11402
Rada AM, Hernández GC, Restrepo E, Villegas MV. Distribución y caracterización molecular de betalactamasas en bacterias Gram negativas en Colombia, 2001-2016. Biomédica. 2019;39:199-220. https://doi.org/10.7705/biomedica.v39i3.4351
Díaz MJ, Amar PW, Angulo LM, BS. Prevalencia de Escherichia coli productor de betalactamasas de espectro extendido (BLEE) y otras resistencias en urocultivos en un hospital general de Ica, Perú. Revista Médica Panacea. 2015;5:20-4. https://doi.org/10.35563/rmp.v5i1.68
Marcos-Carbajal P, Salvatierra G, Yareta J, Pino J, Vásquez N, Díaz P, et al. Caracterización microbiológica y molecular de la resistencia antimicrobiana de Escherichia coli uropatógenas de hospitales públicos peruanos. Rev Peru Med Exp Salud Pública. 2021;38:119-23. https://doi.org/10.17843/ rpmesp.2021.381.6182
Red Latinoamericana de Vigilancia de la Resistencia a los Antimicrobianos (ReLAVRA). Magnitud y tendencias de la resistencia a los antimicrobianos en Latinoamérica. RELAVRA 2014, 2015, 2016. Fecha de consulta: 3 de mayo del 2021. Disponible en: https://bit.ly/2R4PqfT
Mostajo AG, Díaz CA, Morón PR. Frecuencia de infección del tracto urinario intrahospitalaria por enterobacterias productoras de betalactamasas de espectro extendido y factores asociados en un hospital nacional. Revista de la Sociedad Peruana de Medicina Interna. 2015;28:113-20.
Olarte LT, Cáceres GD, Cortés JA. Nuevas cefalosporinas. Rev Chil Infectol. 2018;35:465-75. https://doi.org/10.4067/s0716-10182018000500465
Instituto Geográfico Nacional, 1989. Atlas del Perú. Lima-Perú. Fecha de consulta: 3 de mayo del 2021. Disponible en: https://bit.ly/3y8M2kA
Astete S, Madrid L, Fukuda F, Buckley A, Meritens D, Menchola JV. Sensibilidad antibiótica de los gérmenes causantes de infecciones urinarias en pacientes ambulatorios en el Hospital Nacional Arzobispo Loayza. Rev Soc Per Med Inter. 2004;17:5-8.
Beckman C. MicroScan. Manual de procedimiento para microorganismos gramnegativos, LabPro multirregional ≥ V4.42. U.S.A. August 2019. Fecha de consulta: 3 de mayo de 2021. Disponible en: https://bit.ly/307u5Tq
Clinical & Laboratory Standards Institute. M100: Performance Standards for Antimicrobial Susceptibility Testing, 30th edition. Clinical & Laboratory Standards Institute. Fecha de consulta: 1 de mayo de 2021. Disponible en: https://clsi.org/standards/products/microbiology/documents/m100/
Kiratisin P, Apisarnthanarak A, Laesripa C, Saifon P. Molecular characterization and epidemiology of extended-spectrum-beta-lactamase-producing Escherichia coli and Klebsiella pneumoniae isolates causing health care-associated infection in Thailand, where the CTX-M family is endemic. Antimicrob Agents Chemother. 2008;52:2818-24. https://doi.org/10.1128/AAC.00171-08
Arce Z, Núñez JL, Clavo RF, Valverde DF. Detección del gen CTX-M en cepas de Escherichia coli productoras de β-lactamasas de espectro extendido procedentes del Hospital Regional de Lambayeque; Chiclayo-Perú: noviembre 2012-julio 2013. Revista Del Cuerpo Médico Hospital Nacional Almanzor Aguinaga Asenjo. 2013;6:12-5.
Morejón-García M. Betalactamasas de espectro extendido. Revista Cubana de Medicina. 2013;52:272-80.
García MH, Valdez CA, Porta TV. Detección de los genes de β-lactamasas blaTEM, blaSHV y blaCTX-M en aislamientos de Escherichia coli comunitarios. Revista Científica de la Facultad de Ciencias Químicas y Farmacia. 2019;28:45-56.
Galván F, Agapito J, Bravo N, Lagos J, Tamariz J. Caracterización fenotípica y molecular de Escherichia coli productoras de β-Lactamasas de espectro extendido en pacientes ambulatorios de Lima, Perú. Revista Médica Herediana. 2016;27:22-9.
Alarcón NC, González JF, Sarabia RL, Sánchez JS, Rosas MR. Caracterización de β-lactamasas de espectro extendido producidas por Escherichia coli de infecciones del tracto urinario adquiridas en la comunidad de Chilpancingo. Guerrero, México. 2014. Fecha de consulta: 1 de mayo de 2021. Disponible en: http://tlamati.uagro.mx/t51/t512.pdf
Rodríguez-Villalobos H, Bogaerts P, Berhin C, Bauraing C, Deplano A, Montesinos I, et al. Trends in production of extended-spectrum β-lactamases among Enterobacteriaceae of clinical interest: Results of a nationwide survey in Belgian hospitals. J Antimicrob Chemother. 2011;66:37-47. https://doi.org/10.1093/jac/dkq388
Suárez-Trueba B, Milián-Samper Y, Espinosa-Rivera F, Hart-Casares M, Llanes-Rodríguez N, Martínez-Batista ML. Susceptibilidad antimicrobiana y mecanismos de resistencia de Escherichia coli aisladas a partir de urocultivos en un hospital de tercer nivel. Revista Cubana de Medicina. 2014;53:3-13.
Algunos artículos similares:
- Brian Alejandro Suárez, Claudia Liliana Cuervo, Concepción Judith Puerta, La región intergénica del gen H2A apoya las subpoblaciones KP1(-) y KP1(+) de Trypanosoma rangeli , Biomédica: Vol. 27 Núm. 3 (2007)
- Patricia Escandón, Popchai Ngamskulrungroj, Wieland Meyer, Elizabeth Castañeda, Determinación in vitro de la pareja sexual en aislamientos del complejo Cryptococcus neoformans , Biomédica: Vol. 27 Núm. 2 (2007)
- Isabel Mayorga-Fayad, Gloria I. Lafaurie, Adolfo Contreras, Diana M. Castillo, Alexandra Barón, María del Rosario Aya, Microflora subgingival en periodontitis crónica y agresiva en Bogotá, Colombia: un acercamiento epidemiológico , Biomédica: Vol. 27 Núm. 1 (2007)
- Jessika Consuegra, Sonia Jakeline Gutiérrez, Adriana Jaramillo, Ignacio Sanz, Gilberto Olave, Jorge Enrique Soto, Carlos Valencia, Adolfo Contreras, Bacilos Gram negativos entéricos y no fermentadores de la glucosa en pacientes con enfermedad periimplante , Biomédica: Vol. 31 Núm. 1 (2011)
- Carmelo José Espinosa, Jorge Alberto Cortés, Juan Sebastián Castillo, Aura Lucía Leal, Revisión sistemática de la resistencia antimicrobiana en cocos Gram positivos intrahospitalarios en Colombia , Biomédica: Vol. 31 Núm. 1 (2011)
- Mercedes Figueroa, Armando Cortés, Álvaro Pazos, Luis Eduardo Bravo, Sensibilidad in vitro a amoxicilina y claritromicina de Helicobacter pylori obtenido de biopsias gástricas de pacientes en zona de bajo riesgo para cáncer gástrico , Biomédica: Vol. 32 Núm. 1 (2012)
- Andrea Gómez, Gustavo Salguero, Herbert García, Fabio Aristizábal, Oscar Gutiérrez, Luis Alberto Angel, Jorge Padrón, Carlos Martínez, Humberto Martínez, Omar Malaver, Rosa Barvo, Alejandro Giraldo, Detección de mutaciones de los genes hMLH1 y hMSH2 del sistema de reparación de malos apareamientos del ADN en familias colombianas sospechosas de cancer colorrectal no polipósico hereditario (síndrome de Lynch). , Biomédica: Vol. 25 Núm. 3 (2005)
- Virgilio Galvis, Alejandro Tello, Alfredo Guerra, María Fernanda Acuña, Donaldo Villarreal, Sensibilidad antibiótica de bacterias obtenidas de queratitis e infecciones intraoculares en la Fundación Oftalmológica de Santander (FOSCAL), Floridablanca, Colombia , Biomédica: Vol. 34 (2014): Abril, Suplemento 1, Resistencia bacteriana
- Sandra Yamile Saavedra, Carolina Duarte, María Nilse González, María Elena Realpe, Caracterización de aislamientos de Pseudomonas aeruginosa productores de carbapenemasas de siete departamentos de Colombia , Biomédica: Vol. 34 (2014): Abril, Suplemento 1, Resistencia bacteriana
- Leidy González, Jorge Alberto Cortés, Revisión sistemática de la farmacorresistencia en enterobacterias de aislamientos hospitalarios en Colombia , Biomédica: Vol. 34 Núm. 2 (2014)
| Estadísticas de artículo | |
|---|---|
| Vistas de resúmenes | |
| Vistas de PDF | |
| Descargas de PDF | |
| Vistas de HTML | |
| Otras vistas | |

























